
RNA结合蛋白免疫共沉淀测序技术(RIP-Seq)是研究细胞内RNA与其结合蛋白情况,了解转录后调控网络动态过程的前沿技术。其主要是利用针对特定蛋白的抗体对对应的RNA-蛋白质复合物进行沉淀,再分离复合物后提取结合在复合物上的RNA,并对其进行测序,分析和验证。RIP-Seq可用来了解不同样品中与特定蛋白结合RNA的整体水平,探究结合的RNA的区域或种类和发现miRNA调节靶点等,此技术被广泛的应用在疾病和农业等相关的研究上。
技术路线
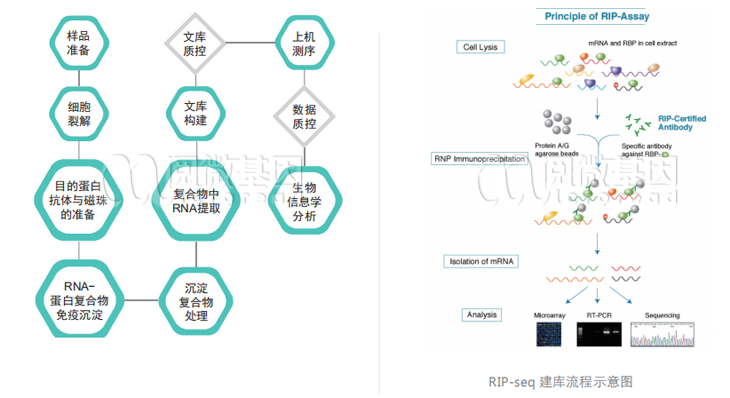
技术优势

测序策略
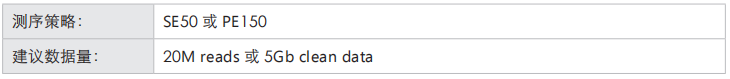
收样要求

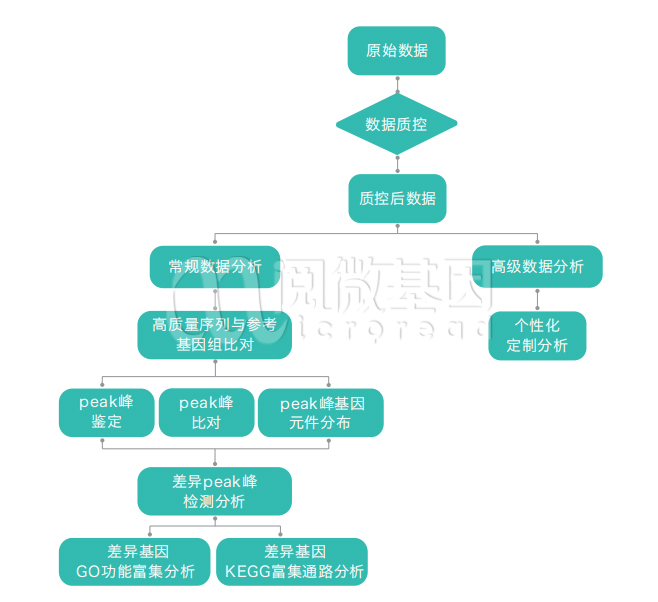
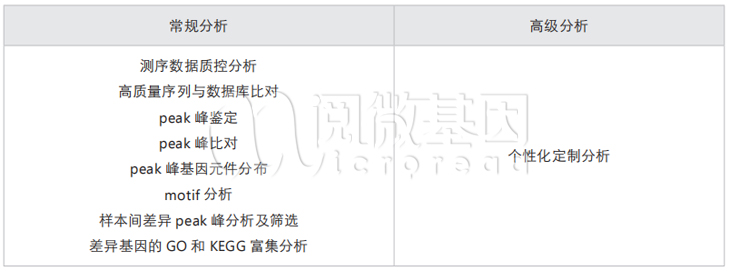
您可以得到的数据分析
案例解析
长链非编码MALAT1通过抑制抑癌因子PCDH10促进胃癌转移
EZH2是多梳蛋白抑制复合体的一个亚基,在癌症的发生发展中常常过度表达,从而在转录过程中沉默抑癌基因,促进癌症发展。很多非编码RNA都可以招募EZH2亚基到特定的组蛋白位点发挥作用。本研究运用RNA免疫共沉淀测序方法研究在人类胃癌中与EZH2亚基相关的RNA,测序后共鉴定出8256个RNA,其中包括了编码mRNAs和非编码RNAs。特别的是,经过分析得知长链非编码RNA:MALAT1可以结合EZH2,并可抑制抑癌因子PCDH10,从而促进胃癌的细胞迁移和浸润。研究通过RIP测序技术与荧光定量技术提供了一个较为全面的与EZH2有关的转录组信息,给胃癌的形成和发展提供了一个新思路。
Qi, Ying, et al. "MALAT1 long ncRNA promotes gastric cancer metastasis by suppressing PCDH10."Oncotarget7.11 (2016): 12693.(Impact factor:5.18)
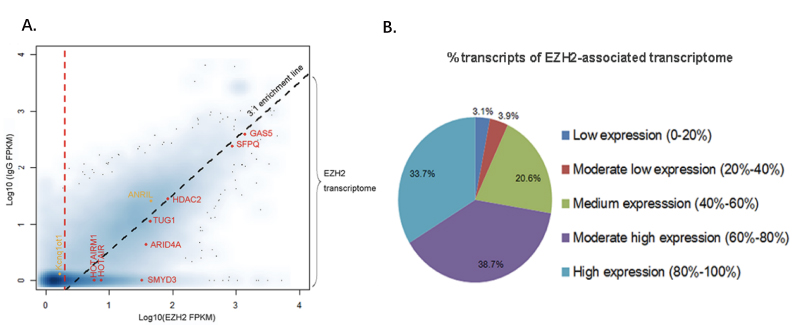
A.EZH2蛋白与对照组IgG蛋白的RIP-seq结果散点图,中间虚线代表3:1 EZH2/IgG富集临界线,红色的点代表通过RIP-Seq获得的样品中目的转录本,橘黄色的点代表已知的与EZH2相关的转录本,但未在本实验中检出。
B.所有在胃癌样品中与EZH2相关的转录本的表达程度饼状图。
胰岛素类mRNA生长因子结合蛋白(IGF2BP3)通过调节miRNA-mRNA相互作用影响恶性肿瘤相关的转录本
IGF2BP3蛋白与恶性肿瘤相关通路存在关系,但是其中的机制却不明确。本研究探究IGF2BP3蛋白与RNA之间的相互作用,通过使用RNA-seq和RIP-seq的方法对胰腺管瘤细胞的两株细胞系(PL45 和PANC1)和对照组(敲除IGF2BP3基因)进行测序,共鉴定出上千个显著差异表达的转录本,结合RIP-seq结果,鉴定出164个与IGF2BP3蛋白直接相关的转录本。通过生物信息学分析,GO和KEGG富集,得知鉴定出的转录本所编码的蛋白与细胞转移、增殖和辅助有紧密联系。敲除IGF2BP3基因减少了胰腺管瘤细胞的入侵性和附着能力。最终结合其他技术如iCLIP 和qRT-PCR等显示出IGF2BP3 通过调节miRNA-mRNA相互作用影响恶性肿瘤相关的转录本。
Ennajdaoui, Hanane, et al. "IGF2BP3 modulates the interaction of invasion-associated transcripts with RISC."Cell reports15.9 (2016): 1876-1883.(impact factor:8.28)
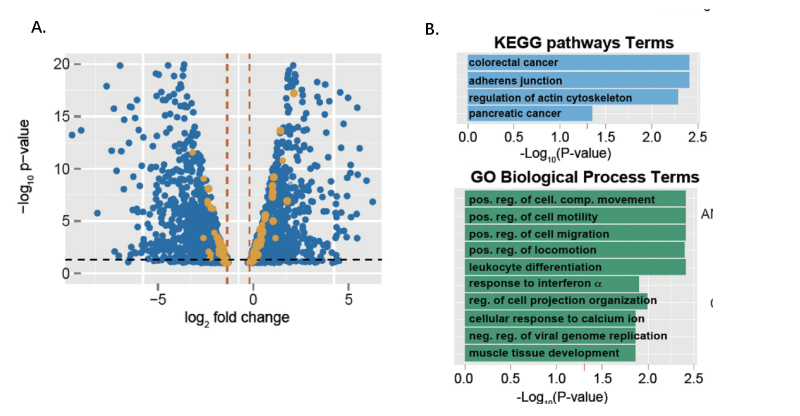
A.RNA-seq和RIP-seq结果火山图。蓝色的点表示在两株不同的细胞系(PL45 和PANC1)中和对照组显著差异表达的基因,橘色点代表通过RIP-seq得出的与IGF2BP3蛋白直接相关的转录本。
B. GO富集和KEGG通路富集,显示得知鉴定出的转录本所编码的蛋白与细胞转移,增殖和辅助有紧密联系。
客户常见问题
物种为2倍体,基因拼接至染色体水平(NCBI),注释完整(GTF文件)的真核生物均可。
RIP-seq实验中的阳性对照和阴性对照是什么?
1. 阳性对照:一般用anti-RNA polymerase II抗体,因为RNA polymerase II是通用转录因子,在所有细胞中都能结合基因的核心启动子区,因此理论上,ChIP后PCR会有条带。一般阳性对照不进行测序。
2. 阴性对照:分为mock和input两种,二者均能起到减少假阳性的作用。mock:用普通IgG为抗体,理论上不会ChIP下来任何DNA片段,因此作为阴性对照。 IgG不需要进行测序,只是判断IP试验中所选取的抗体是否特异。Input是DNA或者RNA片段化后,在进行免疫沉淀前取出一部分断裂后的染色质做input对照(不进行免疫沉淀过程)。Input是断裂后的基因组DNA或者RNA,需要与沉淀后的样品DNA/RNA一起经过逆转交联,DNA/RNA纯化,以及最后的PCR或其他方法检测。通过后续数据分析,我们可以通过input对照排除背景噪音(排除因本底表达水平高或一些非特异性结合所造成的假阳性peaks),验证染色质断裂的效果和整个实验中IP效果。






